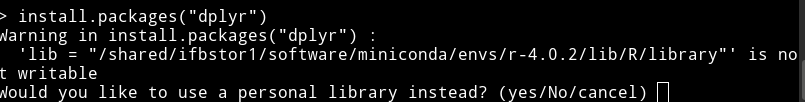
Pouvez vous essayez :
install.packages("dplyr")
Juste avant d'installer le package depuis github.
Il devrait vous poser la question:
et il faut repondre "yes" 2 fois et choisir un mirroir 33 par exemple.
Ensuite re-essayer la commande :
remotes::install_github("...
Je ne sais pas vraiment pourquoi cette derniere ne demande pas elle aussi ou installer les packages.